Dieser Beitrag wurde gemeinsam mit Stephen Aylward, Matt McCormick, Brianna Major von Kitware und Justin Kirby vom Frederick National Laboratory for Cancer Research (FNLCR) verfasst.
Amazon SageMaker Studio Lab bietet kostenloser Zugang zu einer Entwicklungsumgebung für maschinelles Lernen (ML) an jeden mit einer E-Mail-Adresse. Wie das voll ausgestattete Amazon SageMaker Studio, Studio Lab können Sie Ihre eigenen anpassen Conda-Umgebung und CPU- und GPU-skalierbar erstellen JupyterLab Version 3-Notebooks, mit einfachem Zugriff auf die neuesten Data-Science-Produktivitätstools und Open-Source-Bibliotheken. Darüber hinaus sind kostenlose Studio Lab-Konten enthalten mindestens 15 GB persistenter Speicher, sodass Sie Ihre Projekte über mehrere Sitzungen hinweg kontinuierlich pflegen und erweitern können und sofort dort weitermachen können, wo Sie aufgehört haben, und sogar Ihre laufende Arbeit und Arbeitsumgebungen mit anderen teilen können.
Ein zentrales Problem, mit dem sich die Gemeinschaft der medizinischen Bildgebung konfrontiert sieht, besteht darin, wie Forscher in die Lage versetzt werden können, mit diesen wesentlichen Werkzeugen zu experimentieren und zu forschen. Um diese Herausforderung zu lösen, arbeiteten AWS-Teams mit Kitware und Frederick National Laboratory for Cancer Research (FNLCR) um drei wichtige KI-Ressourcen für die medizinische Bildgebung für Studio Lab und die gesamte Open-Source-JupyterLab-Community zusammenzubringen:
Diese Tools und Daten ermöglichen es KI-Forschern in der medizinischen Bildgebung, schnell klinisch einsatzbereite Deep-Learning-Algorithmen in einer umfassenden und benutzerfreundlichen Umgebung zu entwickeln und gründlich zu evaluieren. Teammitglieder von FNLCR und Kitware haben zusammengearbeitet, um eine Reihe von Jupyter-Notebooks zu erstellen, die gängige Arbeitsabläufe für den programmgesteuerten Zugriff auf und die Visualisierung von TCIA-Daten demonstrieren. Diese Notebooks verwenden Studio Lab, damit Forscher die Notebooks ausführen können, ohne ihre eigene lokale Jupyter-Entwicklungsumgebung einrichten zu müssen – Sie können neue Ideen schnell erkunden oder Ihre Arbeit in Präsentationen, Workshops und Tutorials auf Konferenzen integrieren.
Das folgende Beispiel veranschaulicht, wie Studio Lab ein Jupyter-Notebook ausführt, das TCIA-MRT-Daten der Prostata herunterlädt, sie mit MONAI segmentiert und die Ergebnisse mit itkWidgets anzeigt.
Obwohl Sie kleinere Experimente und Demos mit den in diesem Beitrag vorgestellten Beispiel-Notebooks auf Studio Lab kostenlos durchführen können, wird die Verwendung empfohlen Amazon SageMaker-Studio wenn Sie Ihre eigenen medizinischen Bildmodelle in großem Maßstab trainieren. Amazon SageMaker Studio ist eine integrierte webbasierte Entwicklungsumgebung (IDE) mit Sicherheits-, Governance- und Überwachungsfunktionen der Enterprise-Klasse, von der aus Sie auf speziell entwickelte Tools zugreifen können, um alle ML-Entwicklungsschritte durchzuführen. Open-Source-Bibliotheken wie MONAI Core und itkWidgets laufen auch auf Amazon SageMaker Studio.
Installieren Sie die Lösung
Um die TCIA-Notebooks auf Studio Lab auszuführen, müssen Sie ein Konto mit Ihrer E-Mail-Adresse auf der registrieren Studio Lab-Website. Es kann 1–3 Tage dauern, bis Kontoanfragen genehmigt werden.
Danach können Sie den Installationsschritten folgen, um loszulegen:
- Melden Sie sich bei Studio Lab an und starten Sie eine CPU-Laufzeit.
- Navigieren Sie in einem separaten Tab zu TCIA-Notebooks GitHub-Repo und wählen Sie ein Notizbuch im Stammordner des Repositorys aus.
- Auswählen
Öffnen Sie Studio-Lab , um das Notizbuch in Studio Lab zu öffnen.

- Wählen Sie zurück in Studio Lab In Projekt kopieren.

- Wählen Sie im neuen JupyterLab-Popup, das geöffnet wird, aus Ganzes Repo klonen.
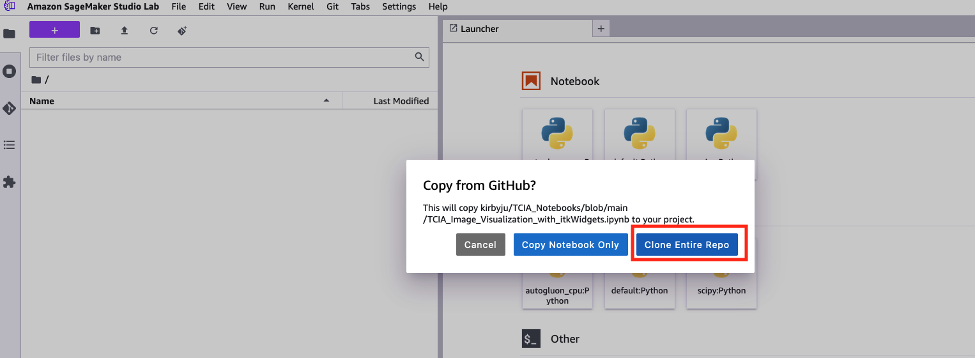
- Behalten Sie im nächsten Fenster die Standardeinstellungen bei und wählen Sie aus Clone.
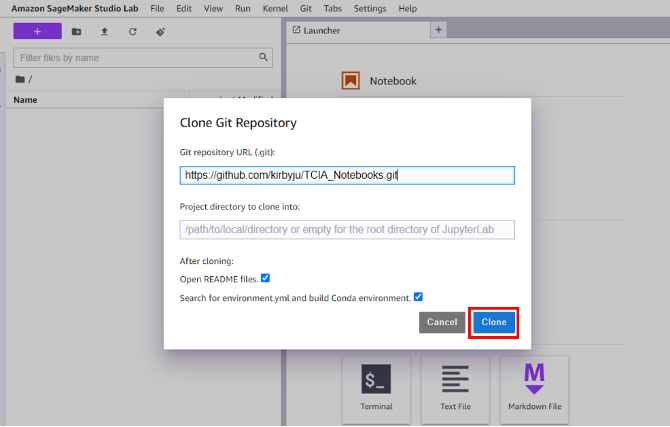
- Auswählen
OK wenn Sie aufgefordert werden, das Erstellen der neuen Conda-Umgebung zu bestätigen (
medical-image-ai).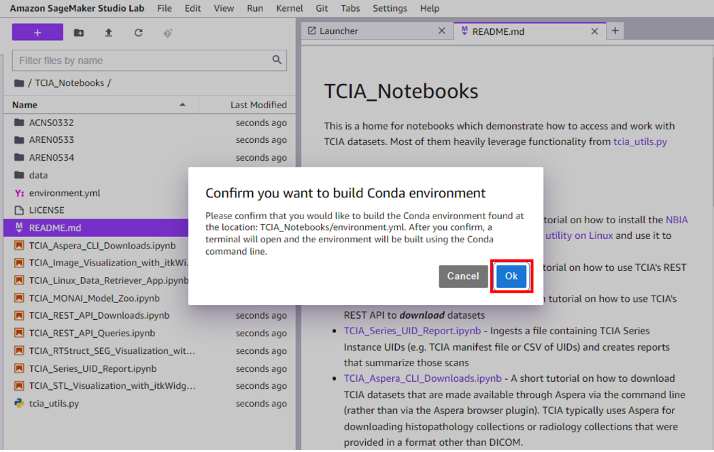 Das Erstellen der Conda-Umgebung dauert bis zu 5 Minuten.
Das Erstellen der Conda-Umgebung dauert bis zu 5 Minuten. - Führen Sie in dem Terminal, das im vorherigen Schritt geöffnet wurde, den folgenden Befehl aus, um NodeJS in der
studiolabConda-Umgebung, die erforderlich ist, um als nächstes die ImJoy JupyterLab 3-Erweiterung zu installieren:conda install -y -c conda-forge nodejs
Wir installieren jetzt die ImJoy Jupyter-Erweiterung mit dem Studio Lab Extension Manager, um interaktive Visualisierungen zu ermöglichen. Die Imjoy-Erweiterung ermöglicht itkWidgets und anderen datenintensiven Prozessen die Kommunikation mit lokalen und entfernten Jupyter-Umgebungen, einschließlich Jupyter-Notebooks, JupyterLab, Studio Lab usw. - Suchen Sie im Extension Manager nach „imjoy“ und wählen Sie aus Installieren.
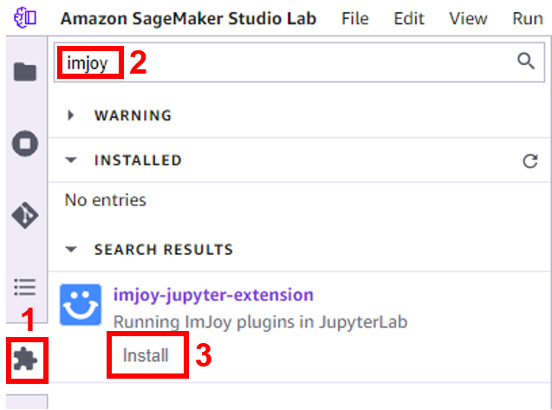
- Bestätigen Sie die Neuerstellung des Kernels, wenn Sie dazu aufgefordert werden.
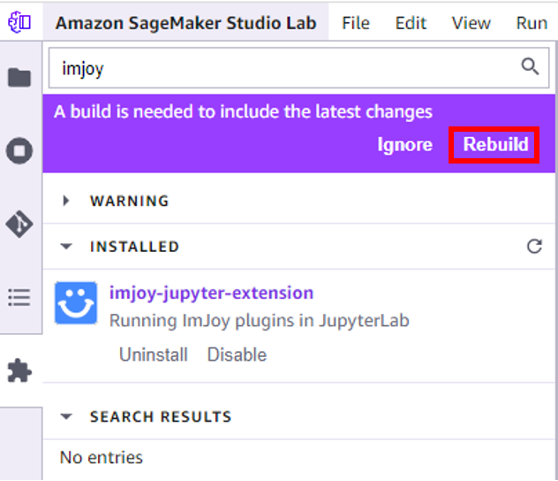
- Auswählen
Speichern und neu laden wenn der Aufbau abgeschlossen ist.
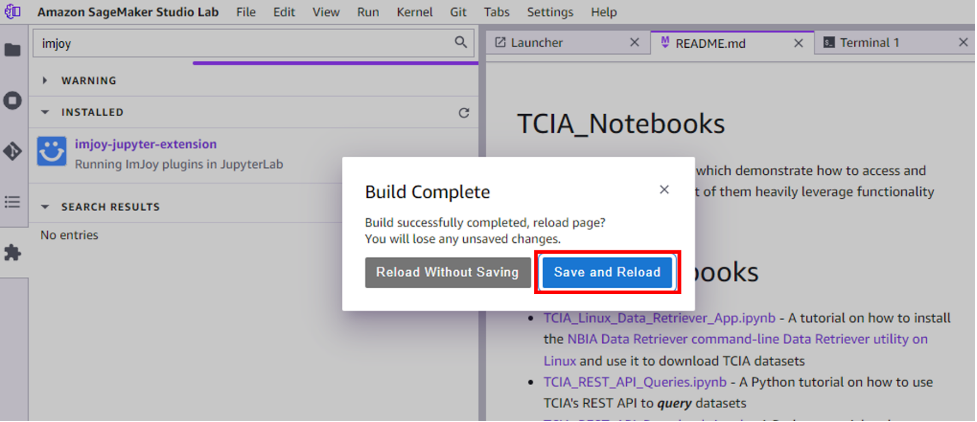
Nach der Installation der ImJoy-Erweiterung können Sie das ImJoy-Symbol im oberen Menü Ihrer Notebooks sehen.
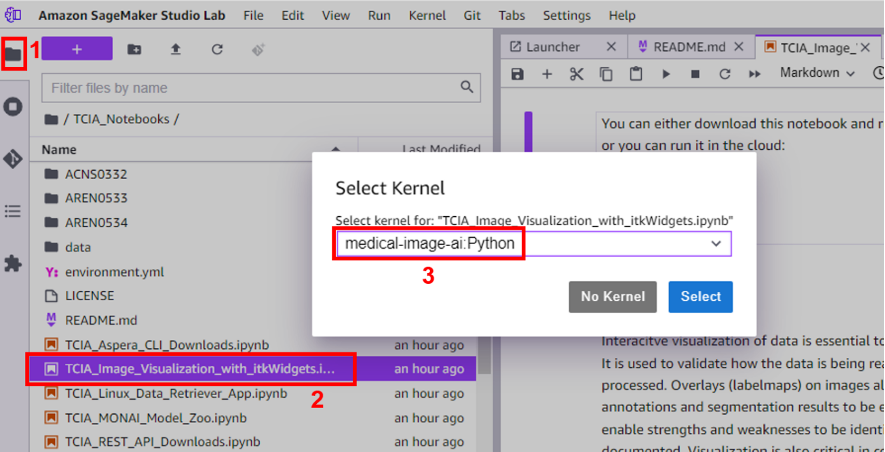
Um dies zu überprüfen, navigieren Sie zum Dateibrowser, wählen Sie die TCIA_Image_Visualalization_with_itkWidgets Notizbuch, und wählen Sie das aus medical-image-ai Kernel, um es auszuführen.
Das ImJoy-Symbol wird in der oberen linken Ecke des Notizbuchmenüs sichtbar sein.
Mit diesen Installationsschritten haben Sie die erfolgreich installiert medical-image-ai Python-Kernel und die ImJoy-Erweiterung als Voraussetzung, um die TCIA-Notebooks zusammen mit itkWidgets auf Studio Lab auszuführen.
Testen Sie die Lösung
Wir haben eine Reihe von Notebooks und ein Tutorial erstellt, die die Integration dieser KI-Technologien in Studio Lab demonstrieren. Achten Sie darauf, die auszuwählen medical-image-ai Python-Kernel beim Ausführen der TCIA-Notebooks in Studio Lab.
Das erste SageMaker-Notizbuch zeigt, wie man DICOM-Bilder von TCIA herunterlädt und diese Bilder mit den filmischen Volume-Rendering-Funktionen von itkWidgets visualisiert.
Das zweite Notizbuch zeigt, wie die Expertenkommentare, die für Hunderte von Studien zu TCIA verfügbar sind, als DICOM SEG- und RTSTRUCT-Objekte heruntergeladen, in 3D oder als Überlagerungen auf 2D-Schnitten visualisiert und für das Training und die Bewertung von Deep-Learning-Systemen verwendet werden können.
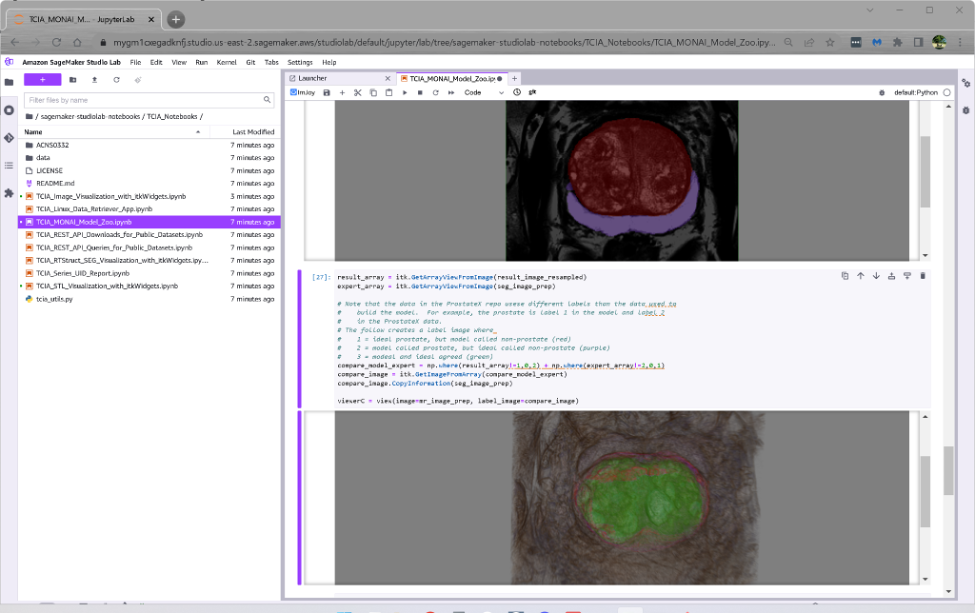
Das dritte Notizbuch zeigt, wie vortrainierte MONAI-Deep-Learning-Modelle, die im Model Zoo von MONAI verfügbar sind, heruntergeladen und verwendet werden können, um TCIA- (oder Ihre eigenen) DICOM-MRT-Volumen der Prostata zu segmentieren.
Auswählen Öffnen Sie Studio-Lab in diesen und anderen JupyterLab-Notebooks, um diese Notebooks in der frei verfügbaren Studio Lab-Umgebung zu starten.
Aufräumen
Nachdem Sie die Installationsschritte in diesem Beitrag befolgt und die medical-image-ai Conda-Umgebung, möchten Sie sie möglicherweise löschen, um Speicherplatz zu sparen. Verwenden Sie dazu den folgenden Befehl:
conda remove --name medical-image-ai --allSie können die ImJoy-Erweiterung auch über den Extension Manager deinstallieren. Beachten Sie, dass Sie die Conda-Umgebung neu erstellen und die ImJoy-Erweiterung neu installieren müssen, wenn Sie später mit den TCIA-Notebooks in Ihrem Studio Lab-Konto weiterarbeiten möchten.
Schließen Sie Ihren Tab und vergessen Sie nicht, auszuwählen Runtime stoppen auf der Studio Lab-Projektseite.
Zusammenfassung
SageMaker Studio Lab ist für medizinische Bild-KI-Forschungsgemeinschaften kostenlos zugänglich und kann für die medizinische Bild-KI-Modellierung und interaktive medizinische Bildvisualisierung in Kombination mit MONAI und itkWidgets verwendet werden. Sie können die offenen Daten von TCIA und Beispiel-Notebooks mit Studio Lab bei Schulungsveranstaltungen wie Hackathons und Workshops verwenden. Mit dieser Lösung können Wissenschaftler und Forscher schnell mit medizinischer Bild-KI experimentieren, zusammenarbeiten und innovativ sein. Wenn Sie über ein AWS-Konto verfügen und eine SageMaker Studio-Domäne eingerichtet haben, können Sie diese Notebooks auch auf Studio ausführen, indem Sie den Standard-Data-Science-Python-Kernel (mit der ImJoy-jupyter-extension installiert) bei der Auswahl aus a Vielzahl von Compute-Instanztypen.
Studio Lab auch hat eine neue Funktion bei AWS re:Invent 2022 eingeführt um die in Studio Lab entwickelten Notebooks zu nehmen und sie als Batch-Jobs nach einem wiederkehrenden Zeitplan in Ihren AWS-Konten auszuführen. Daher können Sie Ihre ML-Experimente über die kostenlosen Rechenbeschränkungen von Studio Lab hinaus skalieren und leistungsfähigere Recheninstanzen mit viel größeren Datensätzen auf Ihren AWS-Konten verwenden.
Wenn Sie mehr darüber erfahren möchten, wie AWS Ihrer Gesundheits- oder Biowissenschaftsorganisation helfen kann, wenden Sie sich bitte an AWS-Vertreter. Für weitere Informationen zu MONAI und itkWidgets kontaktieren Sie bitte Kitware. Neue Daten werden laufend zu TCIA hinzugefügt, und Ihre Vorschläge und Beiträge sind willkommen, indem Sie die besuchen TCIA-Website.
Weiterführende Literatur
Über die Autoren
 Stefan Aylward ist Senior Director of Strategic Initiatives bei Kitware, außerordentlicher Professor für Computer an der University of North Carolina in Chapel Hill und Fellow der MICCAI Society. Dr. Aylward gründete das Büro von Kitware in North Carolina, war Leiter mehrerer Open-Source-Initiativen und ist jetzt Vorsitzender des Beirats von MONAI.
Stefan Aylward ist Senior Director of Strategic Initiatives bei Kitware, außerordentlicher Professor für Computer an der University of North Carolina in Chapel Hill und Fellow der MICCAI Society. Dr. Aylward gründete das Büro von Kitware in North Carolina, war Leiter mehrerer Open-Source-Initiativen und ist jetzt Vorsitzender des Beirats von MONAI.
 Matt McCormick, PhD, ist Distinguished Engineer bei Kitware, wo er die Entwicklung des Insight Toolkit (ITK), eines wissenschaftlichen Bildanalyse-Toolkits, leitet. Er war Hauptprüfer und Mitprüfer mehrerer Forschungsstipendien der National Institutes of Health (NIH), leitete Engagements mit nationalen Labors der Vereinigten Staaten und leitete verschiedene kommerzielle Projekte zur Bereitstellung fortschrittlicher Software für medizinische Geräte. Dr. McCormick ist ein starker Verfechter von Community-gesteuerter Open-Source-Software, Open Science und reproduzierbarer Forschung.
Matt McCormick, PhD, ist Distinguished Engineer bei Kitware, wo er die Entwicklung des Insight Toolkit (ITK), eines wissenschaftlichen Bildanalyse-Toolkits, leitet. Er war Hauptprüfer und Mitprüfer mehrerer Forschungsstipendien der National Institutes of Health (NIH), leitete Engagements mit nationalen Labors der Vereinigten Staaten und leitete verschiedene kommerzielle Projekte zur Bereitstellung fortschrittlicher Software für medizinische Geräte. Dr. McCormick ist ein starker Verfechter von Community-gesteuerter Open-Source-Software, Open Science und reproduzierbarer Forschung.
 Brianna Major ist ein Forschungs- und Entwicklungsingenieur bei Kitware mit einer Leidenschaft für die Entwicklung von Open-Source-Software und -Tools, die der medizinischen und wissenschaftlichen Gemeinschaft zugute kommen.
Brianna Major ist ein Forschungs- und Entwicklungsingenieur bei Kitware mit einer Leidenschaft für die Entwicklung von Open-Source-Software und -Tools, die der medizinischen und wissenschaftlichen Gemeinschaft zugute kommen.
 JUstin Kirby ist technischer Projektmanager am Frederick National Laboratory for Cancer Research (FNLCR). Seine Arbeit konzentriert sich auf Methoden, die den Datenaustausch ermöglichen und gleichzeitig die Privatsphäre der Patienten wahren, um die Reproduzierbarkeit und Transparenz in der Krebsbildgebungsforschung zu verbessern. Sein Team gründete 2010 The Cancer Imaging Archive (TCIA), das die Forschungsgemeinschaft genutzt hat, um über 200 Datensätze zu Manuskripten, Stipendien, Herausforderungswettbewerben und großen NCI-Forschungsinitiativen zu veröffentlichen. Diese Datensätze wurden in über 1,500 Peer-Review-Veröffentlichungen diskutiert.
JUstin Kirby ist technischer Projektmanager am Frederick National Laboratory for Cancer Research (FNLCR). Seine Arbeit konzentriert sich auf Methoden, die den Datenaustausch ermöglichen und gleichzeitig die Privatsphäre der Patienten wahren, um die Reproduzierbarkeit und Transparenz in der Krebsbildgebungsforschung zu verbessern. Sein Team gründete 2010 The Cancer Imaging Archive (TCIA), das die Forschungsgemeinschaft genutzt hat, um über 200 Datensätze zu Manuskripten, Stipendien, Herausforderungswettbewerben und großen NCI-Forschungsinitiativen zu veröffentlichen. Diese Datensätze wurden in über 1,500 Peer-Review-Veröffentlichungen diskutiert.
 Gang-Fu ist Healthcare Solution Architect bei AWS. Er promovierte in pharmazeutischen Wissenschaften an der University of Mississippi und verfügt über mehr als zehn Jahre Erfahrung in Technologie und biomedizinischer Forschung. Er interessiert sich leidenschaftlich für Technologie und die Auswirkungen, die sie auf das Gesundheitswesen haben kann.
Gang-Fu ist Healthcare Solution Architect bei AWS. Er promovierte in pharmazeutischen Wissenschaften an der University of Mississippi und verfügt über mehr als zehn Jahre Erfahrung in Technologie und biomedizinischer Forschung. Er interessiert sich leidenschaftlich für Technologie und die Auswirkungen, die sie auf das Gesundheitswesen haben kann.
 Alex Lemm ist Business Development Manager für medizinische Bildgebung bei AWS. Alex definiert und führt Markteinführungsstrategien mit Bildgebungspartnern durch und treibt die Entwicklung von Lösungen voran, um die KI/ML-basierte medizinische Bildgebungsforschung in der Cloud zu beschleunigen. Er ist begeistert von der Integration von Open-Source-ML-Frameworks mit dem AWS AI/ML-Stack.
Alex Lemm ist Business Development Manager für medizinische Bildgebung bei AWS. Alex definiert und führt Markteinführungsstrategien mit Bildgebungspartnern durch und treibt die Entwicklung von Lösungen voran, um die KI/ML-basierte medizinische Bildgebungsforschung in der Cloud zu beschleunigen. Er ist begeistert von der Integration von Open-Source-ML-Frameworks mit dem AWS AI/ML-Stack.
- SEO-gestützte Content- und PR-Distribution. Holen Sie sich noch heute Verstärkung.
- Platoblockkette. Web3-Metaverse-Intelligenz. Wissen verstärkt. Hier zugreifen.
- Quelle: https://aws.amazon.com/blogs/machine-learning/share-medical-image-research-on-amazon-sagemaker-studio-lab-for-free/
- 1
- 100
- 2D
- 3d
- 77
- a
- Fähig
- Über uns
- beschleunigen
- Zugang
- zugänglich
- Konto
- Trading Konten
- über
- hinzugefügt
- Adresse
- advanced
- beratend
- Beirat
- Anwalt
- Nach der
- AI
- ai Forschung
- AI / ML
- alex
- Algorithmen
- Alle
- Zulassen
- erlaubt
- Amazon
- Amazon Sage Maker
- Amazon SageMaker-Studio
- Amazon SageMaker Studio Lab
- Analyse
- und
- genehmigt
- Archiv
- verfügbar
- AWS
- AWS re: Invent
- Grundlage
- Bevor
- Sein
- Nutzen
- Beyond
- größer
- biomedizinische
- Tafel
- bringen
- Browser
- bauen
- Geschäft
- Geschäftsentwicklung
- Krebs
- Krebsforschung
- Fähigkeiten
- tragen
- Vorsitzende
- challenges
- Auswählen
- Cloud
- zusammenarbeiten
- arbeitete zusammen
- COM
- Kombination
- kombinieren
- kommerziell
- gemeinsam
- mit uns kommunizieren,
- Communities
- community
- Von der Gemeinschaft angetrieben
- Ligen
- abschließen
- umfassend
- Berechnen
- Computer
- Kongressbegleitung
- Schichtannahme
- Kontakt
- fortsetzen
- ständig
- Beiträge
- Kernbereich
- Ecke
- Kosten
- CPU
- erstellen
- erstellt
- anpassen
- technische Daten
- Datenwissenschaft
- Datenübertragung
- Datensätze
- Tage
- tief
- tiefe Lernen
- Standard
- defaults
- Definiert
- zeigen
- Demos
- entwickeln
- entwickelt
- Entwicklung
- Entwicklung
- Geräte
- Direktor
- diskutiert
- Displays
- Distinguished
- Domain
- Nicht
- herunterladen
- Downloads
- leicht
- ermöglichen
- ermöglichen
- Ingenieur
- Unternehmensqualität
- Ganz
- Arbeitsumfeld
- Umgebungen
- essential
- Äther (ETH)
- bewerten
- Auswertung
- Sogar
- Veranstaltungen
- jedermann
- Beispiel
- Führt aus
- ERFAHRUNGEN
- Experiment
- Experte
- ERKUNDEN
- Erweiterung
- konfrontiert
- Merkmal
- funktions
- Eigenschaften
- Kerl
- Reichen Sie das
- Vorname
- konzentriert
- folgen
- gefolgt
- Folgende
- Gründung
- Gerüste
- Frederick
- Frei
- für
- voll
- bekommen
- gif
- GitHub
- Zum Markt gehen
- Governance
- für Balkonkraftwerke Reduzierung
- Hackathons
- Gesundheit
- Gesundheitswesen
- Hilfe
- hält
- Ultraschall
- Hilfe
- HTML
- HTTPS
- hunderte
- ICON
- Ideen
- Image
- Bildanalyse
- Bilder
- Imaging
- Impact der HXNUMXO Observatorien
- zu unterstützen,
- in
- das
- Einschließlich
- Information
- Initiativen
- wir innovieren
- Einblick
- installieren
- installiert
- Instanz
- integrieren
- integriert
- Integration
- Integration
- interaktive
- interessiert
- Problem
- IT
- Jobs
- Jupyter Notizbuch
- Niklas
- Behalten
- Wesentliche
- Labor
- Labor
- neueste
- starten
- Führer
- umwandeln
- lernen
- geführt
- Bibliotheken
- Lebensdauer
- Biowissenschaften
- Einschränkungen
- aus einer regionalen
- Maschine
- Maschinelles Lernen
- halten
- Dur
- um
- Manager
- sowie medizinische
- Medizinprodukte
- medizinische Bildgebung
- Mitglieder
- MENÜ
- Methoden
- Minimum
- Minuten
- Mississippi
- ML
- Modell
- Modellieren
- für
- Überwachung
- mehr
- MRI
- mehrere
- National
- National Institutes of Health
- Navigieren
- Need
- Neu
- neue Funktion
- weiter
- NIH
- Norden
- Nord-Carolina
- Notizbuch
- Laptops
- Objekte
- Office
- laufend
- XNUMXh geöffnet
- offene Daten
- Open-Source-
- Quelloffene Software
- geöffnet
- öffnet
- Organisation
- Andere
- Anders
- besitzen
- Leidenschaft & KREATIVITÄT
- leidenschaftlich
- Vertrauen bei Patienten
- Peer
- ausführen
- Biowissenschaften
- wählen
- Plato
- Datenintelligenz von Plato
- PlatoData
- Bitte
- Pop-up
- Post
- größte treibende
- Presentations
- vorgeführt
- Principal
- Datenschutz
- anpassen
- PRODUKTIVITÄT
- Produktivitätswerkzeuge
- Professor
- Projekt
- Projekte
- bietet
- Bereitstellung
- Publikationen
- veröffentlichen
- Python
- schnell
- RE
- bereit
- empfohlen
- wiederkehrend
- Registrieren
- bezogene
- entfernt
- entfernen
- Rendering
- Quelle
- Zugriffe
- falls angefordert
- Forschungsprojekte
- Forschung und Entwicklung
- Forschungsgemeinschaft
- Forscher
- Downloads
- Die Ergebnisse
- bewertet
- Wurzel
- Führen Sie
- Laufen
- sagemaker
- SageMaker Studio Lab
- Speichern
- Skalieren
- Zeitplan
- Wissenschaft
- WISSENSCHAFTEN
- Wissenschaftler
- Suche
- Zweite
- Sicherheitdienst
- Segment
- Segmente
- Auswahl
- Senior
- getrennte
- Modellreihe
- Sessions
- kompensieren
- mehrere
- Teilen
- ,,teilen"
- Konzerte
- kleinere
- So
- Gesellschaft
- Software
- Lösung
- Lösungen
- LÖSEN
- Quelle
- Raumfahrt
- Stapel
- Anfang
- begonnen
- Staaten
- Schritt
- Johannes
- Shritte
- Lagerung
- Strategisch
- Strategien
- stark
- Es wurden Studien
- Studio Adressen
- Erfolgreich
- Systeme und Techniken
- Nehmen
- Team
- Teams
- Technische
- Technologies
- Technologie
- zehn
- Terminal
- Das
- ihr
- deswegen
- Dritte
- gründlich
- nach drei
- zu
- gemeinsam
- Toolkit
- Werkzeuge
- Top
- Training
- Ausbildung
- Transparenz
- Lernprogramm
- Tutorials
- Vereinigt
- USA
- Universität
- -
- benutzerfreundlich
- verschiedene
- überprüfen
- Version
- sichtbar
- Visualisierung
- visualisieren
- Volumen
- Volumen
- Webbasiert
- willkommen
- welche
- während
- werden wir
- ohne
- Arbeiten
- gearbeitet
- Workflows
- arbeiten,
- Workshops
- Jahr
- Ihr
- Zephyrnet
- ZOO